规模化畜禽养殖能够降低运营成本、方便管理, 逐渐成为我国畜禽养殖业的主体, 但畜禽养殖所带来的环境污染问题却不容忽视.2020年第二次全国污染源普查显示[1], 畜禽养殖业是我国农业源污染物的主要来源, 2017年畜禽养殖业水污染物COD、NH4+-N、总氮和总磷的排放量分别占农业源污染物总量的93.8%、51.3%、42.1%和56.5%.
养殖废水主要由畜禽尿液、部分残余粪便和饲料残渣、圈舍冲洗水等组成, 含有较高浓度有机污染物、氨氮、磷以及悬浮物, 并且伴有恶臭.目前多采用厌氧生物、好氧生物或“厌氧-好氧”联合生物处理技术去除养殖废水中的污染物.杜龑等[2]的研究利用上流式厌氧污泥床(up-flow anaerobic sludge bed, UASB)-序批式活性污泥反应器(sequencing batch reactor, SBR)组合工艺处理畜禽养殖废水, 该工艺对COD、NH4+-N和TN去除率分别达90.87%、98.65%和71.59%.文献[3]提高了养殖废水排放标准, 地方养殖废水标准和水环境质量标准(广东、浙江、四川等)的制订进一步提升了当地养殖废水排放标准或受纳水体的环境质量标准.从养殖废水稳定达标排放的强制要求和保障受纳水体生态系统功能两方面, 需要对经生物处理工艺后的出水, 进一步选用生态处理技术进行深度处理.人工湿地具有运行成本低、易于维护和具有景观效应的优点, 可与生物处理工艺配合作为养殖废水的深度处理工艺进一步净化出水水质[4].普遍认为人工湿地利用基质-微生物-植物生态系统的物理、化学和生物协同作用, 通过过滤、吸附、沉淀、离子交换、植物吸收和微生物分解等多种途径实现对污水[5]包括养殖废水[6~8]的高效净化.
在畜禽养殖生产中, 通常在动物饲料中添加抗生素和重金属等具有杀菌、预防疾病和促生等作用的药剂维持畜禽健康.然而抗生素和重金属等物质难以被畜禽吸收利用, 有30%~70%的药剂以原药或初级代谢物形式被排出动物体外[9], 使得养殖废水除了碳氮磷等常规污染物外, 还含有多种抗生素和重金属等污染物[10].养殖废水中抗生素种类繁多, 典型兽药如四环素类抗生素在废水中被频繁检出, 检出浓度可达μg·L-1~mg·L-1[11~13], 重金属如Cu2+浓度则可达到mg·L-1级别[14].除这些污染物外, 因抗生素滥用所导致抗生素抗性基因(antibiotic resistance genes, ARGs)的潜在传播风险对生态环境和人类健康有着更大的威胁, 多种类型ARGs在养殖废水中被检出, 四环素抗性基因(tetracycline resistance genes, TRGs)几乎有着最高的检出频率[15].抗生素可通过抑制微生物功能基因表达, 影响污水生物处理设施的脱氮除磷功能[16], Chen等[17]的研究表明在2 mg·L-1和5 mg·L-1TC胁迫下, SBR系统的TN去除率由80.2%分别降至69.2%和65.1%.抗生素和重金属对ARGs在环境中的行为特征有重要影响, Zhang等[18]的研究发现在畜禽粪便厌氧消化过程中, Cu2+与抗生素存在共选择作用, 增加了ARGs丰度; Pal等[19]的研究证实, 湿地进水中低浓度Cu2+和Zn2+对湿地土壤中ARGs种类和丰度有长期选择作用, 而且Cu2+的存在增大了ARGs水平基因转移风险[20].人工湿地对养殖废水中的抗生素和ARGs有较明显的去除效果[21], Li等[22]的研究发现人工湿地对养殖废水中抗生素、ARGs的平均去除率分别达45.7%和80.2%.然而有关畜禽养殖废水中抗生素和重金属复合污染对人工湿地去除碳氮磷和削减ARGs功能的综合影响却鲜见报道.因此本研究通过构造潜流人工湿地(人工湿地), 针对实际养殖废水中的碳氮磷常规污染物以及抗生素、ARGs和重金属等特征污染物, 探究人工湿地对这些污染物的去除效果、去除特征以及可能的影响因素, 评估人工湿地用于畜禽养殖废水深度处理和降低养殖废水排水中ARGs传播风险的可行性.
1 材料与方法 1.1 水平潜流人工湿地的构建本实验用水平潜流人工湿地为: 长75.5 cm、宽52.5 cm、高49 cm的矩形结构, 见图 1.利用穿孔板将湿地分为进水区、处理区和出水区这3个部分, 长度分别为8、59.5和8 cm.进水区前端设置高位水池, 通过阀门控制进水流速, 出水区由底部向上间隔15 cm设置2个Φ15 mm出水阀, 用来调节人工湿地水位和排出湿地出水.湿地土壤取自福建省平潭县稻田, 碎石为本地建筑用碎石.湿地进、出水区自上而下依次铺设30 cm厚、粒径10~30 mm的碎石和10 cm厚、粒径3~5 mm的碎石.处理区填料层厚度为40 cm: 上层(0~25 cm)为土壤层, 中层(25~30 cm)为粒径10~30 mm碎石, 下层为粒径(30~40 cm) 3~5 mm碎石; 实验用芦苇采自附近湿地, 选取生长状况基本一致的芦苇移栽至湿地.在湿地处理区一侧种植2株芦苇, 芦苇种植密度为10株·m-2, 芦苇栽种位置见图 2.芦苇根系采用300目尼龙根袋包裹, 湿地另一侧设置同样根袋, 但根袋内不种植芦苇, 用根袋区分芦苇根际及非根际土壤.分别在芦苇根际以及另一侧无植物的根袋内埋设电极(ORP-33C, EA Instruments, UK), 监测芦苇根际及非根际土壤氧化还原电位; 在湿地处理区栽种植物一侧, 距湿地底部20 cm、沿池长布设3个土壤溶液采样器(Rhizon CSS, Φ2.5 mm×10 cm, Rhizosphere, Netherlands), 采集沿程水样, 采样点分别距进水穿孔板8、30和52 cm, 如图 2所示.
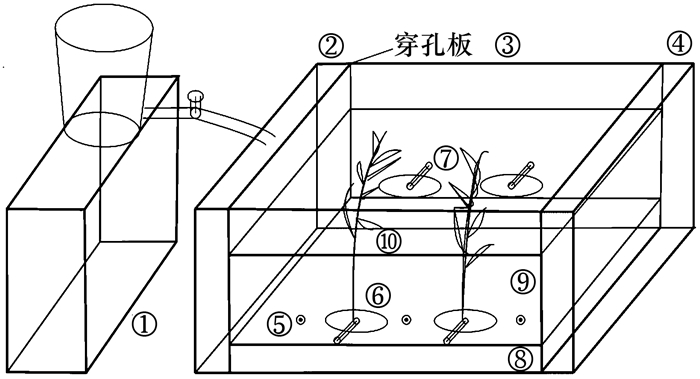
|
①高位水箱; ②进水区; ③处理区; ④出水区; ⑤沿程采样点; ⑥根袋; ⑦电极; ⑧碎石层; ⑨土壤层; ⑩芦苇 图 1 人工湿地装置示意 Fig. 1 Schematic diagram of CWs |

|
图 2 植株和采样布置 Fig. 2 Arrangement diagram of plants and sampling points |
本实验用人工湿地有4组处理: 空白处理即湿地进水为模拟养殖废水(CK); 湿地进水中外源添加1 mg·L-1 TC(TC处理); 湿地进水中外源添加5 mg·L-1 Cu2+(Cu处理); 湿地进水中外源添加1 mg·L-1 TC和5 mg·L-1 Cu2+(TC+Cu处理), 每组处理设置2个平行.湿地进水流量为15 L·d-1, 水力停留时间为5 d.
1.2 进水水质采用商品有机肥(主要原料为猪粪)浸出液配置模拟养殖废水, 将有机肥和自来水按固液比1∶40浸泡12 h得浸出液, 然后稀释浸出液, 并添加葡萄糖、乙酸钠和氯化铵等碳、氮源, 模拟养殖废水中碳、氮和磷污染物浓度.本实验进水水质: ρ(TOC)为(133.3±62.2) mg·L-1, ρ(TN)为(29.0±7.1) mg·L-1, ρ(NH4+-N)为(27.8±7.6) mg·L-1, ρ(NO2--N)为(15.6±14.6) μg·L-1, ρ (NO3--N)为(1.8±0.7) mg·L-1, ρ(PO43--P)为(26.6±11.9) mg·L-1.
1.3 样品采集和测试分析本实验期间, 每周定期采集湿地进水、出水, TOC采用总有机碳分析仪(multiN/C3100, Analytik Jena, Germany)测定; NH4+-N采用纳氏试剂分光光度法(HJ 535-2009)测定, NO2--N采用N-(1-萘基)-乙二胺分光光度法(GB 7493-87)测定, NO3--N采用紫外分光光度法(HJ/T 346-2007)测定, TN采用碱性过硫酸钾紫外分光光度法(HJ 636-2012)测定; PO43--P采用钼酸铵分光光度法(HJ 670-2013)测定.参照DeForest[23]的分析方法, 测定湿地土壤酶活性, 包括磷酸酶、β-葡萄糖苷酶、β-纤维二糖甘酶、乙酰氨基葡萄糖苷酶、β-木糖苷酶、α-葡萄糖甘酶、亮氨酸氨肽酶、酚氧化酶和过氧化物酶; 利用超高效液相色谱串联质谱仪[Waters AcquityTMUPLC串联XevoTMTQ、WatersC18色谱柱(100 mm×2.1 mm, 1.7 μm, Waters, USA)]测定水中TC浓度[24]; 利用原子吸收分光光度计测定水中Cu2+浓度.
1.4 TRGs定量分析分别采集各组湿地出水0.5 L于棕色玻璃瓶, 水样经0.45 μm玻璃纤维滤膜过滤后, 收集滤膜, 按照水样DNA提取试剂盒(Qiagen, Dneasy PowerWater Kit, USA)说明提取DNA.采用微量分光光度计(Thermo NanoDrop 2000c, USA)测定DNA浓度(核酸纯度A260/A280>1.8), 将DNA样品保存于-20℃冰箱.11种TRGs分别为tetA、tetC、tetE、tetG、tetM、tetO、tetQ、tetW、tetT、tetBp和tetX, TRGs及16S rRNA基因引物及退火温度见表 1.使用荧光定量CFX96仪(CFX96Thermocycler Bio-Rad, USA)对目标基因特异性扩增, 反应体系为20 μL: SYBER酶10 μL, 上、下游引物各0.4 μL, 模板DNA 2 μL, 无菌水7.2 μL.定量PCR反应程序为: 5℃预变性5 min, 95℃ 30 s, 退火温度30 s, 72℃ 30 s, 35个循环, 72℃ 5 min, 12℃ 1 min.各基因标准曲线相关系数R2均大于0.99, 扩增效率在90%~120%, 符合定量PCR实验要求, 可用于各TRGs绝对丰度计算.
|
|
表 1 目标基因定量引物序列及退火温度 Table 1 Primer sequences and annealing temperature for target genes of q-PCR |
1.5 数据统计方法
数据处理采用Excel、Origin8.5和SPSS23软件; 污染物去除率计算公式:
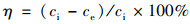
|
式中, ci和ce分别为进水和出水污染物浓度.
2 结果与讨论 2.1 人工湿地植物根际与非根际土壤的氧化还原电位土壤氧化还原电位(oxidation-reduction potential, ORP)用来反映土壤所处的氧化还原状态[31].湿地运行期间芦苇根际及非根际土壤ORP值如图 3所示.在湿地未进水前各组湿地无论是根际土壤还是非根际土壤ORP值均在400~600 mV间, 处于好氧状态[32]; 人工湿地连续运行后, 湿地内部处于淹水状态, 非根际土壤ORP值逐渐降低, 运行17 d后降低至0 mV以下, 随后稳定在-100~0 mV间, 这种受淹水形成的还原状态利于微生物反硝化反应的进行; 与非根际土壤不同, 芦苇根系泌氧作用使根际土壤ORP值稳定在100 mV以上.运行期间, 各组人工湿地根际土壤ORP值始终高于非根际土壤.湿地中厌氧、缺氧和好氧生境为硝化/反硝化细菌提供了良好生境, 有利于微生物硝化和反硝化反应的进行, 为湿地生物脱氮创造了条件.

|
图 3 人工湿地植物根际和非根际土壤ORP值变化 Fig. 3 Variation in ORP in rhizosphere and non-rhizosphere soil in CWs |
自2020年5月起, 人工湿地连续运行, 各组湿地对TOC、NH4+-N、TN和PO43--P的去除率如图 4.模拟养殖废水经人工湿地处理后, CK、TC、Cu和TC+Cu组湿地出水ρ(TOC)分别为7.1~57、9.7~65、8.8~76和10.5~68 mg·L-1, 运行期间4组人工湿地对TOC的去除率在65%~93%之间, CK组人工湿地对TOC的去除效率在70%以上, 这表明人工湿地对养殖废水中含碳有机物有良好的去除效果.人工湿地作为污水生态处理技术, 对污染物的去除性能受季节变化影响较大, 从图 4看出TOC去除率在7月最高, 可达85%~90%以上, 进入11月后, TOC去除率逐步下降至70%.7月是植物生长旺盛期, 南京11月的日均温度为8~16℃, 芦苇开始枯萎, 12月的日均温度降至2~8℃, 湿地中芦苇逐渐衰败.有研究表明, 温度低于15℃, 不利于微生物的生长代谢[33], 植物衰败和微生物活性降低, 导致人工湿地对TOC去除效率降低.CK、TC、Cu和TC+Cu组出水ρ(PO43--P)分别为0.3~11、0.4~13、0.5~12和0.2~16 mg·L-1, 运行初期4组人工湿地对PO43--P去除率可达90%以上, 整个运行期间PO43--P去除率稳定在70%以上.通常认为湿地土壤、基质中含有大量Ca2+、Mg2+和Al3+等离子, 易与废水中的PO43-结合生成磷酸钙和磷酸镁等吸附沉淀在土壤和基质中, 这是人工湿地除磷的主要机制[34, 35].

|
图 4 人工湿地对TOC、NH4+-N、TN和PO43--P的去除效果 Fig. 4 Removal efficiencies of TOC, NH4+-N, TN, and PO43--P of CWs |
CK、TC、Cu和TC+Cu组湿地出水ρ(NH4+-N)分别为2.7~7.9、3.0~9.8、3.8~13.9和4.9~15.4 mg·L-1, 出水ρ(TN)分别为2.6~9.8、4.4~20.3、5.3~17.7和7.3~21.5 mg·L-1.CK组湿地对NH4+-N的去除率可达到74%~90%, 对TN的去除率则在77%~93%.人工湿地主要通过微生物硝化-反硝化作用去除废水中的N[36, 37], Matheson等[38]的研究表明人工湿地通过微生物脱氮去除的TN占总去除率的71%, 湿地植物根系泌氧在潜流湿地内部形成的好氧-缺氧-厌氧交替微环境为硝化和反硝化细菌提供了适宜的氧生境.湿地植物可吸收污水中的营养物质从而去除污染物, 尉中伟等[39]的研究表明湿地栽种芦苇可提高湿地脱氮率, 芦苇地上部分氮吸收量占湿地脱氮量的10.2%.
由图 4可知, 同一运行时间的湿地如TC、Cu和TC+Cu处理下的湿地对TOC、NH4+-N和TN去除率均低于CK组.人工湿地运行初期, 各组湿地对碳氮磷的去除率没有显著差异.运行30 d后, 与CK组相比, 进水中分别添加TC和Cu2+使人工湿地对NH4+-N和TN的去除率显著降低, 进水中添加TC处理使湿地对NH4+-N和TN去除率分别降低了1.5%~16%和0.4%~22%; 进水中添加Cu2+处理使湿地对NH4+-N和TN去除率降低了2.8%~21%和2.5%~25%; TC+Cu组湿地对NH4+-N和TN的去除率分别下降了8.3%~23%和4.2%~37%.
各组湿地对碳氮磷去除率的差异可能与湿地土壤微生物受到TC和Cu2+的持续胁迫有关.Cu2+通过影响土壤微生物的数量及酶活性影响土壤硝化作用和反硝化作用[40].不同处理下湿地的土壤酶活性见表 2, 与CK相比, TC和Cu2+处理均使与碳代谢有关的土壤酶包括酚氧化酶、过氧化物酶、α-葡萄糖甘酶、β-葡萄糖苷酶、β-纤维二糖甘酶和β-木糖苷酶, 与氮代谢有关的土壤酶包括乙酰氨基葡萄糖苷酶、亮氨酸氨肽酶以及与磷代谢有关的磷酸酶等酶活性有所降低, 其中酚氧化酶、β-纤维二糖甘酶、β-木糖苷酶、乙酰氨基葡萄糖苷酶、亮氨酸氨肽酶和磷酸酶等酶活性显著低于CK(P < 0.05).土壤酶活性与污染物去除率相关性见表 3, 通过分析土壤酶活性与污染物去除率相关性, 3组湿地PO43--P去除率与磷酸酶活性均呈显著正相关(P < 0.05), TC组亮氨酸氨肽酶活性与TN去除率、Cu组乙酰氨基葡萄糖苷酶活性与NH4+-N去除率相关系数分别为0.659和0.591.乙酰氨基葡萄糖苷酶和亮氨酸氨肽酶均参与土壤氮代谢循环, 湿地处理废水过程中, TC和Cu2+由废水迁移并累积至湿地土壤和基质层, 会影响湿地土壤微生物群落结构和土壤酶活性等, 从而影响湿地对NH4+-N和TN的去除效果.
|
|
表 2 不同处理对土壤酶活性的影响/nmol·(g·h)-1 Table 2 Effect of different treatments on soil enzyme activities/nmol·(g·h)-1 |
|
|
表 3 土壤酶活性与污染物去除率相关性 Table 3 Correlation between soil enzyme activities and removal efficiencies of pollutants |
2.3 污染物浓度随湿地沿程的变化
人工湿地稳定运行后, 分别在各组湿地进水区、处理区及出水区收集水样, 分析碳氮磷等污染物的沿程变化, 本实验数据取自2020年10月, 如图 5.各组人工湿地处理区前端时, TOC和PO43--P去除率分别可达58%~94%和72%~90%. TOC和PO43--P随水流流经湿地浓度继续降低, 但降低趋势趋于平缓.
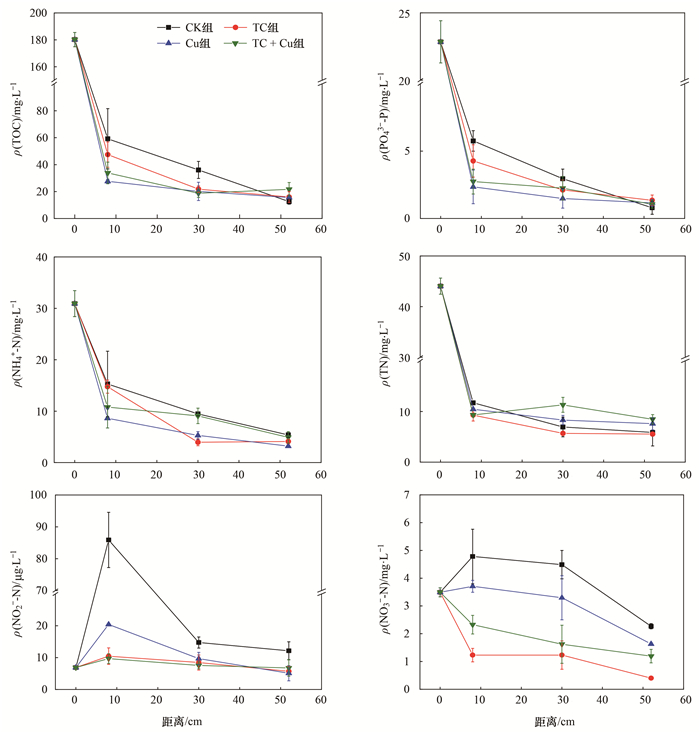
|
图 5 人工湿地污染物浓度沿程变化情况 Fig. 5 Contaminants concentration changes along the length of CWs |
与TOC和PO43--P沿程变化情况类似, 进水ρ(NH4+-N)和ρ(TN)经过处理区前端后均迅速降低, 各组湿地前端对NH4+-N去除率达57%~92%, 对TN的去除率达80%, 湿地前端NH4+-N和TN去除率占到湿地总去除率的60%以上, 甚至可达90%.总体来看, 湿地对NH4+-N和TN的去除具有同步性.不同处理下, 湿地沿程及出水ρ(NO2--N)都较低, 各组湿地进水ρ(NO2--N)在6.9 μg·L-1, 出水ρ(NO2--N)在4.8~7.9 μg·L-1.ρ(NO3--N)除CK组在湿地前端由3.5 mg·L-1升高到4.8 mg·L-1, Cu组在湿地前端由3.5 mg·L-1升高到4.8 mg·L-1, 其余组湿地水样中ρ(NO3--N)沿程呈下降趋势, 出水ρ(NO3--N)在1.2~1.6 mg·L-1.湿地进水中氮主要以NH4+-N形式存在, 湿地沿程和出水水样中ρ(NO2--N)和ρ(NO3--N)较低, 说明微生物的硝化和反硝化过程较协调.进水中的溶解氧和芦苇根部泌氧为湿地前端土壤微生物提供了氧来源, 废水中以NH4+-N为主的含氮污染物可被前端土壤中的硝化细菌等转化成NO2--N和NO3--N, 而人工湿地前端有机负荷高, 为反硝化细菌提供了充足碳源, 造成了水中ρ(TN)和ρ(NH4+-N)在湿地前端迅速下降.
2.4 人工湿地对TC、Cu2+和TRGs的去除效果湿地运行期间分别对进、出水中ρ(TC)和ρ(Cu2+)进行了测定, Cu组和TC+Cu组湿地Cu2+去除率见表 4.实测进水ρ(TC)约800 μg·L-1, ρ(Cu2+)约5~6 mg·L-1.经人工湿地处理后, 出水ρ(TC)降至0.028~0.309 μg·L-1(数据未显示), ρ(Cu2+)降至0.034~1.4 mg·L-1, 人工湿地对TC的去除率可以达到99%, 对Cu2+的去除率维持在90%以上.人工湿地对抗生素的去除方式有基质吸附、植物吸收、微生物降解和水解转化.有研究表明人工湿地对TC的去除率可达85%~95%, 这种高效去除主要通过湿地土壤、基质对TC的吸附截留来实现[41, 42].TC可通过分子间作用力与土壤有机质表面吸附位点相结合, 使TC被吸附在土壤中[43], 在pH近中性条件下, TC可与多种金属阳离子生成不溶性螯合物.人工湿地可通过化学沉淀、植物和微生物吸收等方式去除Cu2+, 湿地内部厌氧环境为硫酸盐还原成S2-提供了有利条件, Cu2+与S2-结合成低溶解性或不溶性沉淀可促使Cu2+的去除[44].
|
|
表 4 人工湿地对Cu2+的去除率/% Table 4 Removal efficiencies of Cu2+ by CWs/% |
为评估人工湿地对废水中TRGs的去除效果, 分别对进水、出水tetA、tetC、tetE、tetG、tetM、tetO、tetQ、tetW、tetT、tetBp和tetX等11种TRGs和16S rRNA基因做了定量检测, 并计算各目标基因绝对丰度.本实验数据取自2020年10月.
4组人工湿地进、出水TRGs和16S rRNA基因绝对丰度(lg)变化如图 6.进水TRGs绝对丰度在7.14×106~4.55×109 copies·L-1, 不同抗性机制基因的绝对丰度有明显差异, 编码四环素外排蛋白基因(tetA、tetC、tetE和tetG)的绝对丰度(7.48×108~4.55×109 copies·L-1)高于编码核糖体保护蛋白基因(tetM、tetO、tetQ、tetBp、tetW和tetT)的绝对丰度(7.14×106~2.15×108 copies·L-1).经湿地处理后, CK、TC、Cu和TC+Cu组湿地出水TRGs绝对丰度分别为9.57×103~8.35×106、1.13×104~1.27×107、8.57×103~8.34×106和8.26×103~1.83×107 copies·L-1, 出水TRGs和16S rRNA基因绝对丰度均显著低于进水(低约2~3个数量级), 人工湿地对TRGs绝对丰度的去除率均在99%以上.

|
图 6 湿地进、出水的TRGs和16S rRNA基因绝对丰度变化 Fig. 6 Changes in absolute abundance of TRGs and 16S rRNA gene in influent or effluent of CWs |
4组人工湿地进、出水TRGs相对丰度变化如图 7.进水TRGs相对丰度在5.7×10-4(tetM)~3.7×10-1(tetE).CK组湿地处理后出水TRGs相对丰度在1.2×10-4(tetBp)~1.0×10-1(tetG), 出水tetA、tetC、tetE、tetO、tetQ、tetT和tetBp基因相对丰度显著低于进水(P < 0.05), CK组湿地对7种TRGs的去除率在43.3%(tetC)~96.3%(tetA)之间.人工湿地对废水中ARGs有良好的去除效果, Liu等[45]的研究利用人工湿地对养殖废水中tetM、tetO和tetW进行处理, 3种基因的去除率均在50%以上.本实验结果表明人工湿地不仅可以有效降低废水中TRGs绝对丰度, 对其相对丰度同样有良好的去除效果.养殖废水在流经人工湿地时, 湿地土壤可通过过滤截留等方式去除水体中的微生物达到去除ARGs的目的[46], Chen等[47]的研究结果显示人工湿地可通过基质吸附截留有效去除废水中ARGs, 去除率可达50.0%~85.5%. Vacca等[48]的研究表明废水经人工湿地处理后出水总细菌数要比进水降低约1.5~2个数量级.
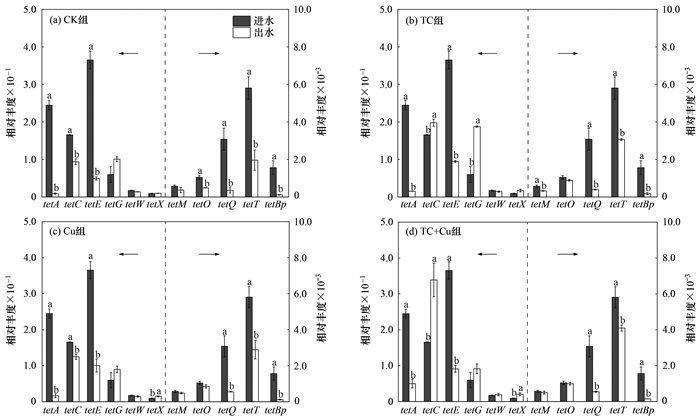
|
图 7 湿地进、出水的TRGs相对丰度变化 Fig. 7 Changes in relative abundance of TRGs in influent or effluent of CWs |
不同处理导致湿地出水TRGs相对丰度有所变化.可能受到Cu2+和TC影响, TC组湿地出水tetC、tetG和tetX相对丰度要明显高于进水, 3种TRGs相对丰度分别比进水提高了16.4%、90.4%和45.9%; TC+Cu组湿地出水tetC、tetG、tetW和tetX基因丰度则比进水高出51.2%、34.7%、11.1%和54.5%; TC、Cu和TC+Cu组出水TRGs相对丰度分别比CK组出水TRGs相对丰度高12%~52%、6.7%~51%和24%~82%.在污水处理系统中, 出水抗性基因丰度不仅与进水中抗性基因丰度有关, 同时也受进水抗生素浓度的影响[49].TRGs丰度与TC浓度之间存在着明显正相关[50].Huang等[51]的研究表明出水TRGs相对丰度会因进水TC浓度增加而提高.养殖废水中微量抗生素及铜、锌对ARGs赋存和进化存在共选择关系, 会增加ARGs丰度和种类[52], Berg等[53]的研究表明由于Cu2+对土壤中微生物抗生素抗性的共选择作用, 微生物群落对四环素的抗性因土壤中Cu2+含量的增加而提高.废水的持续流入, 导致TC和Cu2+累积在湿地土壤, 长期累积在土壤层中的TC和Cu2+在共选择作用下会诱导土壤中微生物抗性基因丰度增加, 这可能导致处理组出水部分TRGs, 如tetC、tetG和tetX相对丰度高于进水以及处理组出水TRGs相对丰度高于CK.
3 结论(1) 受植物根际泌氧影响, 人工湿地植物根际土壤ORP值在100 mV以上, 而非根际土壤ORP值在0 mV以下, 植物根际与非根际土壤氧生境存在明显差异.
(2) 与CK组相比, 进水中添加TC或Cu2+对湿地TN和NH4+-N去除率有明显抑制; 4组人工湿地对TOC、TN、NH4+-N和PO43--P的去除主要发生在湿地前端; 湿地对TC和Cu2+的去除率分别在99.9%和91.4%以上.
(3) 4组湿地对11种TRGs绝对丰度去除率均在99%以上; CK组湿地处理后出水tetA、tetC、tetE、tetO、tetQ、tetT和tetBp等基因相对丰度显著低于进水; 与CK组相比, 进水中添加TC或Cu2+使TC组出水tetC和tetG, Cu组出水tetX和TC+Cu组出水tetC和tetX相对丰度显著高于进水.
| [1] | 中华人民共和国生态环境部, 国家统计局, 中华人民共和国农业农村部. 关于发布《第二次全国污染源普查公报》的公告[EB/OL]. http://www.gov.cn/xinwen/2020-06/10/content_5518391.htm, 2020-06-10/2020-07-26. |
| [2] |
杜龑, 周北海, 袁蓉芳, 等. UASB-SBR工艺处理规模化畜禽养殖废水[J]. 环境工程学报, 2018, 12(2): 497-504. Du Y, Zhou B H, Yuan R F, et al. Treatment of large-scale livestock wastewater by UASB-SBR process[J]. Chinese Journal of Environmental Engineering, 2018, 12(2): 497-504. |
| [3] | 中华人民共和国生态环境部. 畜禽养殖业污染物排放标准(二次征求意见稿)[EB/OL]. https://www.mee.gov.cn/gkml/hbb/bgth/201404/W020140401442973182588.pdf, 2014-03-27. |
| [4] | Faulwetter J L, Gagnon V, Sundberg C, et al. Microbial processes influencing performance of treatment wetlands: a review[J]. Ecological Engineering, 2009, 35(6): 987-1004. DOI:10.1016/j.ecoleng.2008.12.030 |
| [5] | Li Y F, Zhu G B, Ng W J, et al. A review on removing pharmaceutical contaminants from wastewater by constructed wetlands: design, performance and mechanism[J]. Science of the Total Environment, 2014, 468-69: 908-932. |
| [6] | Li X, Wu S H, Yang C P, et al. Microalgal and duckweed based constructed wetlands for swine wastewater treatment: a review[J]. Bioresource Technology, 2020, 318. DOI:10.1016/J.biortech.2020.123858 |
| [7] | Ren B M, Wang T Y, Zhao Y Q. Two-stage hybrid constructed wetland-microbial fuel cells for swine wastewater treatment and bioenergy generation[J]. Chemosphere, 2021, 268. DOI:10.1016/j.chemosphere.2020.128803 |
| [8] | Han Z F, Dong J, Shen Z Q, et al. Nitrogen removal of anaerobically digested swine wastewater by pilot-scale tidal flow constructed wetland based on in-situ biological regeneration of zeolite[J]. Chemosphere, 2019, 217: 364-373. DOI:10.1016/j.chemosphere.2018.11.036 |
| [9] | Qiao M, Ying G G, Singer A C, et al. Review of antibiotic resistance in China and its environment[J]. Environment International, 2018, 110: 160-172. DOI:10.1016/j.envint.2017.10.016 |
| [10] | Yan H C, Zhang K, Shentu J L, et al. Changes to tetracyclines and tetracycline resistance genes in arable soils after single and multiple applications of manure containing tetracyclines[J]. Environmental Science and Pollution Research, 2018, 25(6): 5572-5581. DOI:10.1007/s11356-017-0853-x |
| [11] | Wei R C, Ge F, Huang S Y, et al. Occurrence of veterinary antibiotics in animal wastewater and surface water around farms in Jiangsu Province, China[J]. Chemosphere, 2011, 82(10): 1408-1414. DOI:10.1016/j.chemosphere.2010.11.067 |
| [12] | Ye Z L, Deng Y J, Lou Y Y, et al. Adsorption behavior of tetracyclines by struvite particles in the process of phosphorus recovery from synthetic swine wastewater[J]. Chemical Engineering Journal, 2017, 313: 1633-1638. DOI:10.1016/j.cej.2016.11.062 |
| [13] | Ye Z L, Zhang J Q, Cai J S, et al. Investigation of tetracyclines transport in the presence of dissolved organic matters during struvite recovery from swine wastewater[J]. Chemical Engineering Journal, 2020, 385. DOI:10.1016/j.cej.2019.123950 |
| [14] |
卢信, 罗佳, 高岩, 等. 畜禽养殖废水中抗生素和重金属的污染效应及其修复研究进展[J]. 江苏农业学报, 2014, 30(3): 671-681. Lu X, Luo J, Gao Y, et al. A review in ecotoxic effect of antibiotics and heavy metals co-contamination in livestock and poultry breeding wastewater and its remediation[J]. Jiangsu Journal of Agricultural Sciences, 2014, 30(3): 671-681. DOI:10.3969/j.issn.1000-4440.2014.03.036 |
| [15] | Ben W W, Wang J, Pan X, et al. Dissemination of antibiotic resistance genes and their potential removal by on-farm treatment processes in nine swine feedlots in Shandong Province, China[J]. Chemosphere, 2017, 167: 262-268. DOI:10.1016/j.chemosphere.2016.10.013 |
| [16] | Liao Q, Rong H W, Zhao M H, et al. Interaction between tetracycline and microorganisms during wastewater treatment: a review[J]. Science of the Total Environment, 2021, 757. DOI:10.1016/j.scitotenv.2020.143981 |
| [17] | Chen A, Chen Y, Ding C, et al. Effects of tetracycline on simultaneous biological wastewater nitrogen and phosphorus removal[J]. RSC Advances, 2015, 5(73): 59326-59334. DOI:10.1039/C5RA08434B |
| [18] | Zhang R R, Gu J, Wang X J, et al. Response of antibiotic resistance genes abundance by graphene oxide during the anaerobic digestion of swine manure with copper pollution[J]. Science of the Total Environment, 2019, 654: 292-299. DOI:10.1016/j.scitotenv.2018.11.094 |
| [19] | Pal C, Asiani K, Arya S, et al. Metal resistance and its association with antibiotic resistance[J]. Advances in Microbial Physiology, 2017, 70: 261-313. |
| [20] | Yin Y N, Gu J, Wang X J, et al. Effects of copper addition on copper resistance, antibiotic resistance genes, and intl1during swine manure composting[J]. Frontiers in Microbiology, 2017, 8: 1-10. |
| [21] |
梁惜梅, 聂湘平, 施震. 珠江口典型水产养殖区抗生素抗性基因污染的初步研究[J]. 环境科学, 2013, 34(10): 4073-4080. Liang X M, Nie X P, Shi Z. Preliminary studies on the occurrence of antibiotic resistance genes in typical aquaculture area of the pearl river estuary[J]. Environmetal Science, 2013, 34(10): 4073-4080. |
| [22] | Li S, Zhang R J, Hu J R, et al. Occurrence and removal of antibiotics and antibiotic resistance genes in natural and constructed riverine wetlands in Beijing, China[J]. Science of the Total Environment, 2019, 664: 546-553. DOI:10.1016/j.scitotenv.2019.02.043 |
| [23] | DeForest J L. The influence of time, storage temperature, and substrate age on potential soil enzyme activity in acidic forest soils using MUB-linked substrates and L-DOPA[J]. Soil Biology and Biochemistry, 2009, 41(6): 1180-1186. DOI:10.1016/j.soilbio.2009.02.029 |
| [24] | Jia A, Xiao Y, Hu J Y, et al. Simultaneous determination of tetracyclines and their degradation products in environmental waters by liquid chromatography-electrospray tandem mass spectrometry[J]. Journal of Chromatography A, 2009, 1216(22): 4655-4662. DOI:10.1016/j.chroma.2009.03.073 |
| [25] | Ng L K, Martin I, Alfa M, et al. Multiplex PCR for the detection of tetracycline resistant genes[J]. Molecular and Cellular Probes, 2001, 15(4): 209-215. DOI:10.1006/mcpr.2001.0363 |
| [26] | Huang M H, Zhang W, Liu C, et al. Fate of trace tetracycline with resistant bacteria and resistance genes in an improved AAO wastewater treatment plant[J]. Process Safety and Environmental Protection, 2015, 93: 68-74. DOI:10.1016/j.psep.2014.04.004 |
| [27] | Aminov R I, Garrigues-Jeanjean N, Mackie R I. Molecular ecology of tetracycline resistance: development and validation of primers for detection of tetracycline resistance genes encoding ribosomal protection proteins[J]. Applied and Environmental Microbiology, 2001, 67(1): 22-32. DOI:10.1128/AEM.67.1.22-32.2001 |
| [28] | Luo Y, Mao D Q, Rysz M, et al. Trends in antibiotic resistance genes occurrence in the Haihe River, China[J]. Environmental Science & Technology, 2010, 44(19): 7220-7225. |
| [29] | Ghosh S, Ramsden S J, LaPara T M. The role of anaerobic digestion in controlling the release of tetracycline resistance genes and class 1 integrons from municipal wastewater treatment plants[J]. Applied Microbiology and Biotechnology, 2009, 84(4): 791-796. DOI:10.1007/s00253-009-2125-2 |
| [30] | Duan Q J, Shang S Q, Wu Y D. Rapid diagnosis of bacterial meningitis in children with fluorescence quantitative polymerase chain reaction amplification in the bacterial 16S rRNA gene[J]. European Journal of Pediatrics, 2009, 168(2): 211-216. DOI:10.1007/s00431-008-0747-5 |
| [31] | Rinklebe J, Antić-Mladenović S, Frohne T, et al. Nickel in a serpentine-enriched Fluvisol: redox affected dynamics and binding forms[J]. Geoderma, 2016, 263: 203-214. DOI:10.1016/j.geoderma.2015.09.004 |
| [32] |
杨钙仁, 童成立, 肖和艾, 等. 水分控制下的湿地沉积物氧化还原电位及其对有机碳矿化的影响[J]. 环境科学, 2009, 30(8): 2381-2386. Yang G R, Tong C L, Xiao H A, et al. Effects of water content on redox potential and carbon mineralization of wetland sediments[J]. Environmental Science, 2009, 30(8): 2381-2386. DOI:10.3321/j.issn:0250-3301.2009.08.034 |
| [33] |
廖雪珂, 严晗璐, 王智源, 等. 低温季节水平潜流和垂直潜流人工湿地尾水深度处理中试[J]. 环境科学, 2020, 41(12): 5509-5517. Liao X K, Yan H L, Wang Z Y, et al. Advanced treatment of tail water using pilot-scale horizontal and vertical subsurface flow constructed wetlands in low-temperature seasons[J]. Environmental Science, 2020, 41(12): 5509-5517. |
| [34] | Vohla C, Kōiv M, Bavor H J, et al. Filter materials for phosphorus removal from wastewater in treatment wetlands-A review[J]. Ecological Engineering, 2011, 37(1): 70-89. DOI:10.1016/j.ecoleng.2009.08.003 |
| [35] | Park J H, Kim S H, Delaune R D, et al. Enhancement of phosphorus removal with near-neutral pH utilizing steel and ferronickel slags for application of constructed wetlands[J]. Ecological Engineering, 2016, 95: 612-621. DOI:10.1016/j.ecoleng.2016.06.052 |
| [36] | Vymazal J. The use of hybrid constructed wetlands for wastewater treatment with special attention to nitrogen removal: a review of a recent development[J]. Water Research, 2013, 47(14): 4795-4811. DOI:10.1016/j.watres.2013.05.029 |
| [37] | Paranychianakis N V, Tsiknia M, Kalogerakis N. Pathways regulating the removal of nitrogen in planted and unplanted subsurface flow constructed wetlands[J]. Water Research, 2016, 102: 321-329. DOI:10.1016/j.watres.2016.06.048 |
| [38] | Matheson F E, Sukias J P. Nitrate removal processes in a constructed wetland treating drainage from dairy pasture[J]. Ecological Engineering, 2010, 36(10): 1260-1265. DOI:10.1016/j.ecoleng.2010.05.005 |
| [39] |
尉中伟, 王晓昌, 郑于聪, 等. 水平潜流人工湿地脱氮功效中植物的作用[J]. 环境工程学报, 2015, 9(2): 595-602. Yu Z W, Wang X C, Zheng Y C, et al. Role of plants in horizontal subsurface flow constructed wetlands for nitrogen removal[J]. Chinese Journal of Environmental Engineering, 2015, 9(2): 595-602. |
| [40] |
李平, 郎漫, 李煜姗, 等. 施用猪粪条件下重金属对土壤氮素净转化的影响[J]. 土壤通报, 2017, 48(2): 467-473. Li P, Lang M, Li Y S, et al. Effects of heavy metals on net nitrogen transformation in soil with pig manure applied[J]. Chinese Journal of Soil Science, 2017, 48(2): 467-473. |
| [41] | Song H L, Zhang S, Guo J H, et al. Vertical up-flow constructed wetlands exhibited efficient antibiotic removal but induced antibiotic resistance genes in effluent[J]. Chemosphere, 2018, 203: 434-441. DOI:10.1016/j.chemosphere.2018.04.006 |
| [42] | Du L, Zhao Y Q, Wang C, et al. Removal performance of antibiotics and antibiotic resistance genes in swine wastewater by integrated vertical-flow constructed wetlands with zeolite substrate[J]. Science of the Total Environment, 2020, 721. DOI:10.1016/j.scitotenv.2020.137765 |
| [43] | Teixidó M, Granados M, Prat M D, et al. Sorption of tetracyclines onto natural soils: data analysis and prediction[J]. Environmental Science and Pollution Research, 2012, 19(8): 3087-3095. DOI:10.1007/s11356-012-0954-5 |
| [44] | Šíma J, Svoboda L, Pomijová Z. Removal of selected metals from wastewater using a constructed wetland[J]. Chemistry & Biodiversity, 2016, 13(5): 582-590. |
| [45] | Liu L, Liu C X, Zheng J Y, et al. Elimination of veterinary antibiotics and antibiotic resistance genes from swine wastewater in the vertical flow constructed wetlands[J]. Chemosphere, 2013, 91(8): 1088-1093. DOI:10.1016/j.chemosphere.2013.01.007 |
| [46] | Liu X H, Guo X C, Liu Y, et al. A review on removing antibiotics and antibiotic resistance genes from wastewater by constructed wetlands: performance and microbial response[J]. Environmental Pollution, 2019, 254. DOI:10.1016/j.envpol.2019.112996 |
| [47] | Chen J, Wei X D, Liu Y S, et al. Removal of antibiotics and antibiotic resistance genes from domestic sewage by constructed wetlands: optimization of wetland substrates and hydraulic loading[J]. Science of the Total Environment, 2016, 565: 240-248. DOI:10.1016/j.scitotenv.2016.04.176 |
| [48] | Vacca G, Wand H, Nikolausz M, et al. Effect of plants and filter materials on bacteria removal in pilot-scale constructed wetlands[J]. Water Research, 2005, 39(7): 1361-1373. DOI:10.1016/j.watres.2005.01.005 |
| [49] | Peak N, Knapp C W, Yang R K, et al. Abundance of six tetracycline resistance genes in wastewater lagoons at cattle feedlots with different antibiotic use strategies[J]. Environmental Microbiology, 2007, 9(1): 143-151. DOI:10.1111/j.1462-2920.2006.01123.x |
| [50] | Wu N, Qiao M, Zhang B, et al. Abundance and diversity of tetracycline resistance genes in soils adjacent to representative swine feedlots in China[J]. Environmental Science & Technology, 2010, 44(18): 6933-6939. |
| [51] | Huang X, Liu C X, Li K, et al. Performance of vertical up-flow constructed wetlands on swine wastewater containing tetracyclines and tet genes[J]. Water Research, 2015, 70: 109-117. DOI:10.1016/j.watres.2014.11.048 |
| [52] | Poole K. At the nexus of antibiotics and metals: the impact of Cu and Zn on antibiotic activity and resistance[J]. Trends in Microbiology, 2017, 25(10): 820-832. DOI:10.1016/j.tim.2017.04.010 |
| [53] | Berg J, Thorsen M K, Holm P E, et al. Cu exposure under field conditions coselects for antibiotic resistance as determined by a novel cultivation-independent bacterial community tolerance assay[J]. Environmental Science & Technology, 2010, 44(22): 8724-8728. |
 2021, Vol. 42
2021, Vol. 42


