2. 常州市疾病预防控制中心, 常州 213022;
3. 江苏省常州环境监测中心, 江苏省环境保护水环境生物监测重点实验室, 常州 213001
2. Changzhou Centers for Disease Control and Prevention, Changzhou 213022, China;
3. Key Laboratory of Environmental Protection of Water Environment Biological Monitoring of Jiangsu Province, Changzhou Environmental Monitoring Center of Jiangsu Province, Changzhou 213001, China
抗生素是用来预防和治疗细菌感染的药物, 长期以亚治疗剂量添加于动物饲料中以预防动物疾病和刺激动物生长[1, 2].据统计, 我国每年兽用抗生素使用量高达9万t, 约占年产抗生素原料的一半[3].当抗生素进入动物体内, 会诱导产生抗性菌株, 提供潜在的抗性传播储库[4]; 而由动物肠道排出的耐药菌, 会通过移动遗传元件驱动抗生素抗性基因(antibiotic resistance genes, ARGs)水平转移[5]; 同时, 大部分抗生素作为未代谢的母体化合物也会随动物粪便和尿液排出体外, 对粪便和尿液中的细菌耐药性具有选择压力[6]; 这些都加剧了养殖环境中ARGs的传播和扩散.目前, 在集约化养殖环境的粪便、土壤、废水和周边环境中检出多种ARGs, 主要检出种类有四环素类、磺胺类和大环内酯类ARGs等[1~4].
为了满足对肉类产品不断增长的需求, 我国家禽生产行业已形成集约化养殖模式, 以提高效率并降低生产成本[7].据联合国统计, 家禽集中饲养占集约化动物养殖场的72%, 根据世界观察研究所的统计数据, 2000~2016年畜禽饲养数量上升60%, 增至240亿只, 其中大部分鸡肉是由集约化饲养场生产[8].而家禽集中在小型密闭空间中, 每天产生大量含有高浓度微生物的动物粪便, 在粪便处理和动物移动期间很容易被气溶胶化[9], 而集约化家禽饲养场所也被认为是室外空气污染的重要点源, 可能对公共健康造成严重问题[7].
近来, 研究者们越来越关注集约化养殖环境空气中ARGs的环境风险[9], 但目前关于该方面的研究还较少, 且较多集中于总悬浮颗粒物(total suspended particulate, TSP)中ARGs的检测[7, 10, 11]和生物气溶胶中耐药菌携带ARGs种类的研究[12~15].细颗粒物(PM2.5)不仅可显著影响空气质量、能见度、人类健康和地球气候, 由于其可以深入渗透到人肺的肺泡区域从而更有可能是ARGs向人体暴露的重要途径[3]. Xie等[16]研究了工业-城市-农村地区PM2.5中ARGs的年度差异, 并统计了ARGs与移动遗传元件(intI1)的关系, 结果表明PM2.5在ARGs的环境传播和人体暴露途径中具有重要意义.本文对集约化肉鸡饲养场舍内PM2.5和粪便以及舍外PM2.5中ARGs进行研究, 以期为集约化家禽饲养环境中ARGs的传播及环境风险提供研究基础, 并评价集约化饲养场PM2.5对人体健康和环境污染的潜在危害.
1 材料与方法 1.1 样品来源与采集采样地点位于常州市某集约化肉鸡饲养场(119°29′26″E, 31°48′59″N), 鸡舍内分为公鸡区和母鸡区, 各饲养5 000只, 密度为14只·m-2.肉鸡类型为黄麻鸡, 存栏时间约为75d, 出栏后进行粪便清理, 采样时鸡龄为52d.养殖室内相对密闭, 通风方式为自然通风.
采样时间为2018年2月, 采集样本包括PM2.5颗粒物和粪便.其中PM2.5颗粒物分别采集于鸡舍内母鸡区(C1-PM2.5)、公鸡区(C2-PM2.5), 舍外20 m处(C3-PM2.5)和舍外50 m处(C4-PM2.5); 粪便样品采集于鸡舍内母鸡区(C1-F)和公鸡区(C2-F), 每类采集3份作为平行样品.颗粒物采样仪器为中流量崂应2050型智能空气采样器(青岛崂山应用技术研究所), PM2.5的采集采用多级切割组合(崂应1071型TSP/PM10/PM2.5采样头, 青岛崂山应用技术研究所), 流量设定为100 L ·min-1.采样所用滤膜为石英滤膜(φ90 mm, Pall Life Science), 滤膜在采样前均使用马弗炉500℃煅烧5 h进行灭菌, 之后用铝箔纸包装将其放入密封袋中.采样前, 采样头、镊子和膜托均用75%酒精进行擦拭.待采样完成后立即将滤膜运回实验室称重并计算PM2.5质量浓度(为防止微生物污染, 滤膜在运回实验室后未进行恒温恒湿处理[17]), 之后将滤膜保存于- 20℃, 用于后续DNA提取.
1.2 DNA提取DNA提取所用试剂盒为DNeasy PowerSoil Kit(Qiagen, Germany), 参考文献[11]将每类采集的3份平行样本分别混合后进行DNA提取.空气样品用无菌牙刷签小心刮取表层滤膜并保证取样完整, 后用灭菌的剪刀将刮取的表层膜尽量剪碎, 再加入到试剂盒提供的研磨珠套管, 并按照试剂盒说明书方法提取样品总DNA; 粪便样品直接按照试剂盒说明书方法提取样品总DNA.使用NanoDrop2000超微量蛋白质核酸分析仪(Thermo Fisher, USA)测定提取DNA的质量浓度和纯度, 将提取成功的DNA置于- 20℃中保存.
1.3 荧光定量检测实时定量PCR(quantitative real-time PCR, qPCR)用于测定肉鸡饲养场PM2.5和粪便DNA样品的总细菌基因(16S rDNA)、一类整合子的整合酶基因(intI1)和针对6类抗生素的19种ARGs:磺胺类(sul1、sul2、sul3)、四环素类(tetA、tetW和tetX)、大环内酯类(ermB、ermC)、喹诺酮类(qnrS、qnrA、qepA)、β-内酰胺类(ampC、blaTEM-1、blaOXA-1、blaOXA-2、blaGES-1、blaSHV-1)和氨基糖苷类(aacC2、aacC3), 相关的引物序列、退火温度和目的基因长度参照文献[18, 19].
使用Bio-Rad iQ5实时荧光定量PCR仪(Bio-Rad, USA)产生阳性对照的校准标准曲线[9], 标准曲线扩增效率在92.1%~108.8%之间.之后利用标准曲线分析各类样品的DNA以评估样品中qPCR抑制剂的存在并确定合适的模板DNA的质量浓度.所有qPCR测定在96孔板中进行, 试验中使用的qPCR反映体系为20 μL, 包括0.20 μmol ·L-1的正向引物和反向引物各0.4 μL, 10 μL的2×TransStartTM Top Green q-PCR SuperMix(TransGen, 北京), 1 μL模板DNA和8.2 μL灭菌超纯水. qPCR反映程序参照文献[19], 每个样品做3个平行, 标准偏差小于0.3, 每次设置阴性对照.
1.4 数据分析将目的基因达到设定阈值所经历的循环数(Ct)代入相应基因的校准标准曲线以计算相应基因的绝对丰度.本试验数据经Origin(2017版)和R语言(2.5.1版)处理并绘制图形. Spearman相关系数运用SPSS(22.0版)计算, 显著性水平设定为P<0.01和P<0.05.
2 结果与讨论 2.1 肉鸡饲养场PM2.5质量浓度及16S rDNA丰度由于所研究肉鸡饲养场鸡舍内相对密闭, 空气密度大, PM2.5质量浓度分别高达643.67 μg ·m-3(母鸡区)和989.03 μg ·m-3(公鸡区), 见图 1.导致两区域PM2.5质量浓度有所差异的原因可能是公鸡较母鸡更为活跃, 在动物活动期间使密闭鸡舍内的废物气溶胶化的程度更大.母鸡区和公鸡区PM2.5质量浓度分别超过《环境空气质量标准》(GB 3095-2012)规定日均值浓度的8倍和13倍, 同时超过《世卫组织空气质量准则》规定日均值浓度的25倍和39倍[20].长期暴露于集约化养殖舍内空气, 会给动物和人类带来许多健康问题[9]; 据报道, 与其他农业工人相比, 家禽饲养工人的眼睛疾病、呼吸系统疾病、皮肤病的患病率更高[21].舍外PM2.5质量浓度相比舍内显著降低(P<0.01), 舍外20 m和50 m处PM2.5质量浓度分别为130.30 μg ·m-3和106.73 μg ·m-3(图 1), 约为以往研究的1.46~1.78倍[22].

|
图 1 肉鸡饲养场PM2.5质量浓度和16S rDNA丰度 Fig. 1 PM2.5 mass concentration and 16S rDNA abundance from the broiler feeding operation |
经qPCR测定, 养殖舍内母鸡区和公鸡区PM2.5中16S rDNA丰度分别为9.75×108 copies ·m-3和2.13×109copies ·m-3(图 1); 较以往关于中国蛋鸡和肉鸡舍内空气中16S rDNA检出丰度高出2~3个数量级[11], 这主要是由于两处养殖环境的通风换气系统、温度、湿度及粪便处理方式都有所差异. Ling等[23]比较了集中动物饲养舍内环境(猪和奶牛)、人类居住的室内环境(诊所和收容所)和室外环境(城市、半城市、畜牧业和高山森林地区)气溶胶样品的16S rDNA丰度, 发现集中动物饲养舍内气溶胶中16S rDNA丰度显著高于另外两类环境(P<0.01).本研究中舍外20 m和50 m处PM2.5中16S rDNA丰度较养殖舍内低2~3个数量级(图 1), 与以往关于养殖舍内空气中16S rDNA检出丰度相当[11, 23].经分析, PM2.5质量浓度与16S rDNA丰度呈显著正相关(P<0.01), 可见集约化肉鸡饲养环境是高浓度空气传播细菌的来源, 会对饲养人员健康和周边空气环境造成危害.
2.2 肉鸡饲养场PM2.5和粪便中ARGs丰度及多样性经qPCR对肉鸡饲养场PM2.5和粪便中intI1和19种ARGs进行定量检测.除blaGES-1和blaSHV-1之外, 其余17种ARGs在六类样品中均有检出(图 2), 部分种类在各类集约化养殖环境的土壤[1, 2]、水体[2, 24]和空气[10~15, 23]中也均有分布.在鸡舍粪便中检出的ARGs种类, 也均存在于PM2.5样品中, 而粪便中未检出的ARGs, 在舍内和舍外PM2.5中也均未检出, 揭示粪便可能是PM2.5中ARGs的重要来源, 而舍内PM2.5也会传播至舍外, 并在风力的作用下将源于饲养场环境的PM2.5进行远距离传播[3]. PM2.5由于粒径小、在大气中的存留时间长、传播距离远[25], 使集约化饲养场所成为环境中ARGs污染的重要点源[23].将6类样品中ARGs/16S rDNA, 即各样品中ARGs的相对丰度进行相关性分析(表 1), 结果显示粪便与PM2.5中ARGs相对丰度均呈显著正相关(P<0.01), 进一步表明粪便是该肉鸡饲养场PM2.5中ARGs的主要来源.
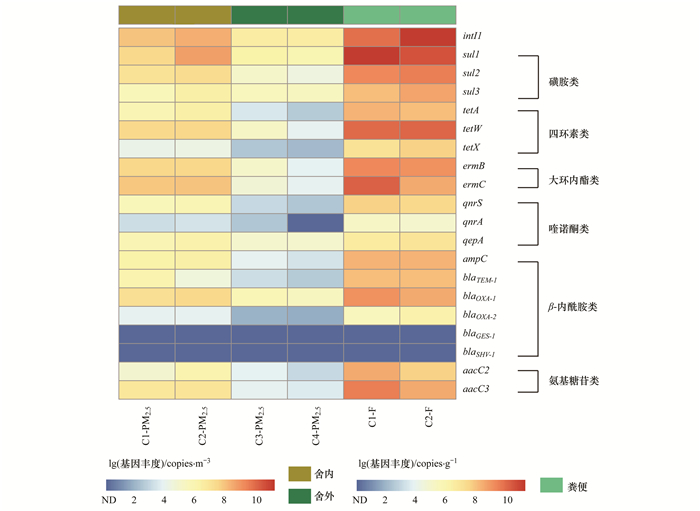
|
图 2 肉鸡饲养场PM2.5和粪便中ARGs丰度分布 Fig. 2 Distribution of ARGs abundance in PM2.5 and feces from the broiler feeding operation |
|
|
表 1 肉鸡饲养场PM2.5和粪便中ARGs/16S rDNA的相关性分析1) Table 1 Correlation analysis of ARGs/16S rDNA between PM2.5 and feces from the broiler feeding operation |
经qPCR测定, 舍内粪便中磺胺类、四环素类、大环内酯类和氨基糖苷类抗性基因丰度较高, 达到1.04×109~3.27×1010 copies ·g-1(图 3), 主要原因可能是饲料中添加相应的抗生素, 并且该肉鸡饲养场粪便清理周期较长.据研究发现四环素类、磺胺类和大环内酯类抗生素是集约化家禽饲养业中最常用的抗生素种类, 而相应的抗性基因种类在动物粪便中普遍存在, 丰度达到2.44×107~7.29×109 copies ·g-1[1, 26].在此次研究的粪便样品中, 母鸡区和公鸡区的ARGs丰度有所差异, 但最高相差不超过1个数量级(图 2). sul1和tetW平均丰度最高, 分别为(9.54±8.57)×1010 copies ·g-1和(1.09±0.28)×1010 copies ·g-1; sul2、ermB、ermC和aacC3平均丰度均超过109 copies ·g-1; blaOXA-2和qnrA平均丰度相对较低, 分别为(8.89±8.92)×105 copies ·g-1和(1.07±0.33)×105 copies ·g-1; 其余检出ARGs的丰度在6.25×106~6.93×108 copies ·g-1之间.
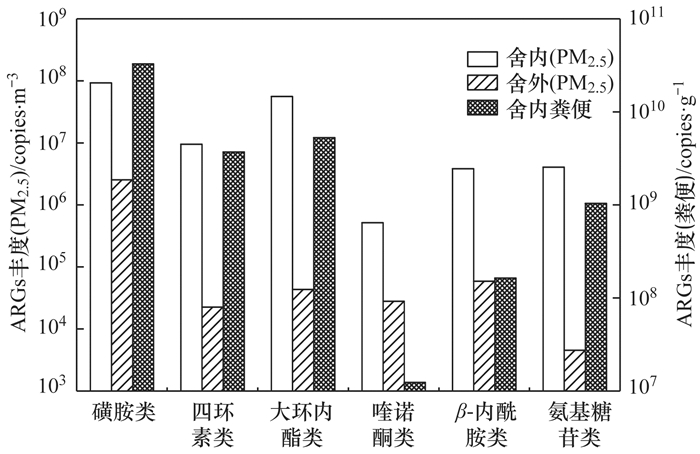
|
图 3 肉鸡饲养场PM2.5和粪便中6类ARGs的平均丰度 Fig. 3 Average abundance of six types of ARGs in PM2.5 and feces from the broiler feeding operation |
如图 2所示, 鸡舍内PM2.5中相应ARGs丰度明显高于舍外PM2.5样品, 对应的ARGs种类, 舍内与舍外丰度相差1~4个数量级.除blaTEM-1外, 鸡舍内公鸡区PM2.5中相应的ARGs丰度均高于母鸡区, 这主要是由于两区域PM2.5质量浓度有所差异(图 1).舍内PM2.5中平均丰度最高的为磺胺类和大环内酯类抗性基因, 分别达到(8.9±1.9)×107 copies ·m-3和(5.6±3.1)×107 copies ·m-3, 其余检出4类ARGs的丰度在5.14×105~9.50×106 copies ·m-3之间, 且舍内PM2.5中6类ARGs丰度变化与粪便中一致(图 3).随着距离的增加, 舍外50 m处ARGs检出丰度较20 m处有所减少(图 2); 除磺胺类抗性基因的平均丰度为(1.6±0.93)×106 copies ·m-3, 其余5类检出ARGs在舍外PM2.5样品中的丰度在4.52×103~5.58×104 copies ·m-3之间(图 3), 表明含有ARGs的PM2.5可以有效转移至附近的环境[9].有研究表明源自肉牛饲养厂的颗粒物(TSP)也会促进兽用抗生素和含有ARGs的细菌群落的传播[10]. Gao等[9]采用8级Andersen采样器进行采样以研究生物气溶胶粒度分布对ARGs的影响, 结果表明ARGs更倾向于分布在粒径更大的颗粒物中.本研究在集约化肉鸡饲养场PM2.5中检出多种ARGs, 与以往关于TSP及生物气溶胶中的ARGs研究(涉及鸡、牛和猪饲养场)相比, 涉及种类较多、检出丰度较高[3, 10~15, 23], 而由此释放到环境中的PM2.5可能对抗生素耐药性的传播产生重大而深远的影响.
2.3 ARGs丰度与intI1丰度、PM2.5质量浓度的相关性作为传播抗生素抗性的主要参与者, intI1在集约化养殖环境的土壤, 粪便、废水及空气中均有检出[11, 23, 27~29].本研究中, 6类样品中的intI1丰度均高于其它ARGs, 这与以往关于堆肥厂大气环境中的研究结果一致[30].公鸡粪便中intI1丰度高达1.83×1011 copies ·g-1, 在舍内PM2.5样品中丰度在108 copies ·m-3左右, 而在舍外PM2.5样品中丰度也均超过106 copies ·m-3(图 2).抗生素抗性环境传播的一个重要机制就是水平基因转移, 而集约化家禽饲养环境则很有可能是intI1的重要储存库[23].
有研究表明1类整合子标记基因intI1与多重耐药性相关[23], 而多重耐药基因的出现和传播给重大疾病的治疗提出了严峻的挑战[31].经分析, 除blaTEM-1丰度与intI1丰度呈显著正相关(r=0.886, P<0.05), 其余检出ARGs丰度均与intI1丰度呈显著正相关(r>0.99, P<0.01), 表明intI1在ARGs的传播中起重要作用(图 4).可见, 该肉鸡饲养场PM2.5中intI1与ARGs存在密切关联, 而这种共存关系可能是由于集约化饲养环境中普遍存在的intI1中存在多个ARGs[30].同时, PM2.5质量浓度越高, intI1和ARGs丰度也越高(P<0.01), 表明该肉鸡饲养场PM2.5可作为多药耐药性的储库.因为空气中的微生物通常附着在颗粒物表面[17], 而高浓度的PM2.5可能会导致高丰度的ARGs及intI1.
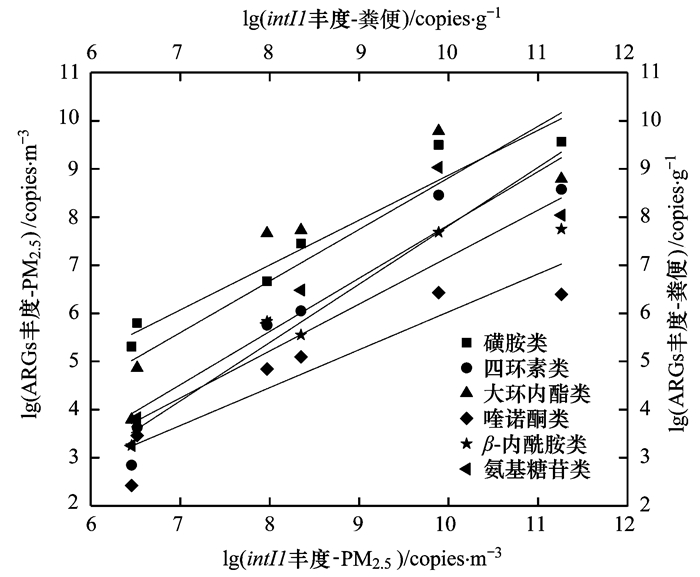
|
图 4 6类ARGs丰度与intI1丰度的关系 Fig. 4 Relationship between the abundance of six types of ARGs and intI1 |
(1) 经qPCR检测, 除blaGES-1和blaSHV-1之外, 其余17种ARGs在肉鸡饲养场PM2.5和粪便样品中均有分布, 而粪便是养殖环境PM2.5中ARGs的主要来源.
(2) 所研究的集约化肉鸡饲养场中PM2.5是空气传播细菌的来源以及intI1和ARGs的重要储存库.
(3) ARGs与intI1的共存关系表明PM2.5可以作为养殖环境多药耐药性的储库, 同时PM2.5是ARGs和intI1进行传播的重要媒介, 可能对饲养人员及家禽健康和周边空气环境造成重要影响.
致谢: 感谢南开大学环境科学与工程学院罗义老师课题组对本研究提供的帮助.| [1] | Ben W W, Wang J, Pan X, et al. Dissemination of antibiotic resistance genes and their potential removal by on-farm treatment processes in nine swine feedlots in Shandong Province, China[J]. Chemosphere, 2017, 167: 262-268. DOI:10.1016/j.chemosphere.2016.10.013 |
| [2] | Wang J, Ben W W, Yang M, et al. Dissemination of veterinary antibiotics and corresponding resistance genes from a concentrated swine feedlot along the waste treatment paths[J]. Environment International, 2016, 92-93: 317-323. DOI:10.1016/j.envint.2016.04.020 |
| [3] |
薛银刚, 刘菲, 王利平, 等. 气溶胶中抗生素抗性基因研究进展:以养殖场和医院为例[J]. 生态毒理学报, 2017, 12(6): 27-37. Xue Y G, Liu F, Wang L P, et al. Progress in research on antibiotic resistance genes in aerosols:take farms and hospitals as examples[J]. Asian Journal of Ecotoxicology, 2017, 12(6): 27-37. |
| [4] | Wu N, Qiao M, Zhang B, et al. Abundance and diversity of tetracycline resistance genes in soils adjacent to representative swine feedlots in China[J]. Environmental Science & Technology, 2010, 44(18): 6933-6939. |
| [5] | Pal C, Bengtsson-Palme J, Kristiansson E, et al. The structure and diversity of human, animal and environmental resistomes[J]. Microbiome, 2016, 4: 54. DOI:10.1186/s40168-016-0199-5 |
| [6] |
隋倩雯, 张俊亚, 魏源送, 等. 畜禽养殖过程抗生素使用与耐药病原菌及其抗性基因赋存的研究进展[J]. 生态毒理学报, 2015, 10(5): 20-34. Sui Q W, Zhang J Y, Wei Y S, et al. Veterinary antibiotics use, occurrence of antibiotic resistance pathogen and its antibiotic resistance genes in animal production:an overview[J]. Asian Journal of Ecotoxicology, 2015, 10(5): 20-34. |
| [7] | Hong P Y, Li X Z, Yang X F, et al. Monitoring airborne biotic contaminants in the indoor environment of pig and poultry confinement buildings[J]. Environmental Microbiology, 2012, 14(6): 1420-1431. DOI:10.1111/j.1462-2920.2012.02726.x |
| [8] | The Guardian. Rise of mega farms: how the US model of intensive farming is invading the world[EB/OL].https://www.theguardian.com/environment/2017/jul/18/rise-of-mega-farms-how-the-us-model-of-intensive-farming-is-invading-the-world?CMP=Share_AndroidApp_Tweet, 2017-07-18. |
| [9] | Gao M, Jia R Z, Qiu T L, et al. Size-related bacterial diversity and tetracycline resistance gene abundance in the air of concentrated poultry feeding operations[J]. Environmental Pollution, 2017, 220: 1342-1348. |
| [10] | McEachran A D, Blackwell B R, Hanson J D, et al. Antibiotics, bacteria, and antibiotic resistance genes:aerial transport from cattle feed yards via particulate matter[J]. Environmental Health Perspectives, 2015, 123(4): 337-343. DOI:10.1289/ehp.1408555 |
| [11] |
高敏, 仇天雷, 秦玉成, 等. 养鸡场空气中抗性基因和条件致病菌污染特征[J]. 环境科学, 2017, 38(2): 510-516. Gao M, Qiu T L, Qin Y C, et al. Sources and pollution characteristics of antibiotic resistance genes and conditional pathogenic bacteria in concentrated poultry feeding operations[J]. Environmental Science, 2017, 38(2): 510-516. |
| [12] | Sapkota A R, Ojo K K, Roberts M C, et al. Antibiotic resistance genes in multidrug-resistant Enterococcus spp. and Streptococcus spp. recovered from the indoor air of a large-scale swine-feeding operation[J]. Letters in Applied Microbiology, 2006, 43(5): 534-540. DOI:10.1111/lam.2006.43.issue-5 |
| [13] | Liu D J, Chai T J, Xia X Z, et al. Formation and transmission of Staphylococcus aureus (including MRSA) aerosols carrying antibiotic-resistant genes in a poultry farming environment[J]. Science of the Total Environment, 2012, 426: 139-145. DOI:10.1016/j.scitotenv.2012.03.060 |
| [14] | Létourneau V, Nehmé B, Mériaux A, et al. Human pathogens and tetracycline-resistant bacteria in bioaerosols of swine confinement buildings and in nasal flora of hog producers[J]. International Journal of Hygiene and Environmental Health, 2010, 213(6): 444-449. DOI:10.1016/j.ijheh.2010.09.008 |
| [15] | Just N A, Létourneau V, Kirychuk S P, et al. Potentially pathogenic bacteria and antimicrobial resistance in bioaerosols from cage-housed and floor-housed poultry operations[J]. The Annals of Occupational Hygiene, 2012, 56(4): 440-449. |
| [16] | Xie J W, Jin L, Luo X S, et al. Seasonal disparities in airborne bacteria and associated antibiotic resistance genes in PM2.5 between urban and rural sites[J]. Environmental Science & Technology Letters, 2018, 5(2): 74-79. |
| [17] | Cao C, Jiang W J, Wang B Y, et al. Inhalable microorganisms in Beijing's PM2.5 and PM10 pollutants during a severe smog event[J]. Environmental Science & Technology, 2014, 48(3): 1499-1507. |
| [18] | Mao D Q, Yu S, Rysz M, et al. Prevalence and proliferation of antibiotic resistance genes in two municipal wastewater treatment plants[J]. Water Research, 2015, 85: 458-466. DOI:10.1016/j.watres.2015.09.010 |
| [19] | Tan L, Li L Y, Ashbolt N, et al. Arctic antibiotic resistance gene contamination, a result of anthropogenic activities and natural origin[J]. Science of the Total Environment, 2018, 621: 1176-1184. DOI:10.1016/j.scitotenv.2017.10.110 |
| [20] | Xiao K, Wang Y K, Wu G, et al. Spatiotemporal characteristics of air pollutants (PM10, PM2.5, SO2, NO2, O3, and CO) in the inland basin city of Chengdu, Southwest China[J]. Atmosphere, 2018, 9(2): 74. DOI:10.3390/atmos9020074 |
| [21] | Just N, Kirychuk S, Gilbert Y, et al. Bacterial diversity characterization of bioaerosols from cage-housed and floor-housed poultry operations[J]. Environmental Research, 2011, 111(4): 492-498. DOI:10.1016/j.envres.2011.01.009 |
| [22] | Ye Z L, Li Q, Ma S S, et al. Summertime day-night differences of PM2.5 components (inorganic ions, OC, EC, WSOC, WSON, HULIS, and PAHs) in Changzhou, China[J]. Atmosphere, 2017, 8(10): 189. |
| [23] | Ling A L, Pace N R, Hernandez M T, et al. Tetracycline resistance and Class 1 integron genes associated with indoor and outdoor aerosols[J]. Environmental Science & Technology, 2013, 47(9): 4046-4052. |
| [24] | He L Y, Ying G G, Liu Y S, et al. Discharge of swine wastes risks water quality and food safety:antibiotics and antibiotic resistance genes from swine sources to the receiving environments[J]. Environment International, 2016, 92-93: 210-219. DOI:10.1016/j.envint.2016.03.023 |
| [25] |
靳璐滨, 臧增亮, 潘晓滨, 等. PM2.5和PM2.5~10资料同化及在南京青奥会期间的应用试验[J]. 中国环境科学, 2016, 36(2): 331-341. Jin L B, Zang Z L, Pan X B, et al. Data assimilation and application experiments of PM2.5 and PM2.5~10 during Nanjing Youth Olympic Games[J]. China Environmental Science, 2016, 36(2): 331-341. DOI:10.3969/j.issn.1000-6923.2016.02.003 |
| [26] | Luby E M, Moorman T B, Soupir M L. Fate and transport of tylosin-resistant bacteria and macrolide resistance genes in artificially drained agricultural fields receiving swine manure[J]. Science of the Total Environment, 2016, 550: 1126-1133. DOI:10.1016/j.scitotenv.2016.01.132 |
| [27] | Zhang Y J, Li H C, Gu J, et al. Effects of adding different surfactants on antibiotic resistance genes and intI1 during chicken manure composting[J]. Bioresource Technology, 2016, 219: 545-551. DOI:10.1016/j.biortech.2016.06.117 |
| [28] | Qian X, Sun W, Gu J, et al. Variable effects of oxytetracycline on antibiotic resistance gene abundance and the bacterial community during aerobic composting of cow manure[J]. Journal of Hazardous Materials, 2016, 315: 61-69. DOI:10.1016/j.jhazmat.2016.05.002 |
| [29] | Cheng W X, Chen H, Su C, et al. Abundance and persistence of antibiotic resistance genes in livestock farms:a comprehensive investigation in eastern China[J]. Environment International, 2013, 61: 1-7. DOI:10.1016/j.envint.2013.08.023 |
| [30] | Gao M, Qiu T L, Sun Y M, et al. The abundance and diversity of antibiotic resistance genes in the atmospheric environment of composting plants[J]. Environment International, 2018, 116: 229-238. DOI:10.1016/j.envint.2018.04.028 |
| [31] | WHO. WHO Director-general delivers lecture at Georgetown university's global futures initiative[EB/OL].http://www.who.int/dg/speeches/2015/georgetown-university-lecture/en/, 2015-09-30. |
 2019, Vol. 40
2019, Vol. 40


