2. 广东省污染控制与修复材料工程技术中心, 广州 510630
2. Guangdong Engineering Center for Environment Contamination Control and Restorative Materials, Guangzhou 510630, China
近些年来,高效去除水体氮素是当前的研究热点[1].与传统生物脱氮技术相比,异养硝化-好氧反硝化脱氮技术可同步去除氨氮和COD,有效缩短了反应途径,且脱氮效率更高、 反应速率更快,因而受到更多的关注.异养硝化-好氧反硝化菌强化系统脱氮效果较好,在强化过程中系统运行状况决定处理效果的高低及出水水质的好坏,而系统内微生物的群落结构和多样性可在一定程度上反映系统的运行状况[2, 3].同时,环境因子如温度、 pH和进水成分等会影响系统微生物群落结构的变化,对处理效果影响十分明显[4, 5, 6].因此,研究系统中微生物群落结构的演替过程及其与环境因子的关系,对于阐明系统内微生物群落结构的组成及提高系统处理效率和稳定运行具有重要的现实意义.
近年来分子生物学发展迅速,尤其是基于16S rDNA的分子生物学方法能有效克服传统微生物分离培养技术的局限,为研究微生物群落结构提供了一个极其重要的手段[7, 8, 9, 10, 11].国内外学者利用该技术对复杂环境中的微生物群落结构进行研究均取得了一定的成果[12, 13, 14].然而,目前以异养硝化-好氧反硝化菌为对象,研究其群落结构的演替过程及其与环境因子之间的关系鲜见报道,对反应器内异养硝化-好氧反硝化菌群结构动态变化的研究则更少.因此,本研究将前期实验制备所得的包埋固定化异养硝化-好氧反硝化菌Burkholderia sp. YX02投加到连续流反应器中建立生物强化系统,利用PCR-DGGE技术分析不同阶段下反应器中微生物的群落结构及其动态演替过程,并对不同阶段微生物结构进行聚类分析和主成分分析以及环境因子与群落结构的相关性分析,以阐明微生物群落的演替与反应器运行状况的动态联系.这对优化反应器运行及提高处理效果具有重要意义,同时能更好地指导实际应用,以期为废水生物脱氮强化处理提供参考.
1 材料与方法 1.1 实验材料包埋固定化异养硝化-好氧反硝化菌 Burkholderia sp. YX02为前期实验制备所得[15].包 埋球粒径约3-4 mm,同时球粒的硬度和机械强度也较高,符合实验要求.
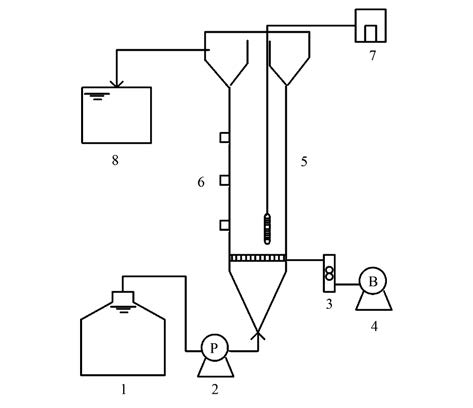
1.2 实验装置与运行实验装置如图 1所示,直径为8 cm、 高为40 cm、 有效容积为1.5 L,采用向上流连续进水,气水同向运行.通过实验已确定其最佳运行条件:进水C/N为10、 pH为7.0左右、 温度为25℃左右、 进气量为4.5 L ·min-1、 进水流量为0.5 L ·d-1.接种污泥取自广州市大坦沙污水处理厂好氧池,投加量约为0.5 L,包埋固定化Burkholderia sp. YX02菌投加量为80 g ·L-1.启动时,将包埋菌Burkholderia sp. YX02与污泥混匀后一并投加于反应器.实验采用人工合成进水,水质组分见表 1.
|
1.进水槽; 2.蠕动泵; 3.流量计; 4.气泵; 5.反应器; 6.排泥口; 7.恒温棒; 8.出水槽 图 1 实验装置示意 Fig. 1 Schematic diagram of experimental set-up |
|
|
表 1 人工合成进水水质 Table 1 Characteristics of the artificially synthesized water fed to activated sludge reactor |
反应器保持连续运行,且每隔两天取污泥样品用于细菌DNA的提取,期间共取样品9份,分别记为S1-S9.相应地采集反应器出水,并测定pH、 NH4+-N、 NO2--N、 NO3--N和COD的值.
1.4 细菌基因组DNA的提取取25 mL活性污泥加入到100 mL锥形瓶中,120 r ·min-1下振荡10 min以使污泥被打散均匀.取污泥10 mL于15 mL的离心管内,8 000 r ·min-1下离心10 min,弃去上清液,收集沉淀污泥.重复上述操作一次,取5 mL污泥进行细菌总DNA提取.具体提取步骤参考文献[16, 17]提出的方法,所用试剂盒购自上海生工.将提取的细菌总DNA一部分于-20℃保存,另一部分在0.7%的琼脂糖凝胶中做电泳检测,并将电泳条带进行扫描拍照.
1.5 PCR-DGGEPCR引物的选择采用对大多数细菌和古细菌16S rDNA基因V3区具有特异性的引物对[18],即F357-GC和R518. PCR反应体系和反应条件参照陈谊等[19]提出的方法确定.建立50 μL PCR反应体系: 1.5 μL dNTP(25 mmol ·L-1),1.5 μL引物F357-GC,1.5 μL引物R518,2.5 μL Taq酶,5 μL 10× buffer(含Mg2+),1 μL DNA模板,37 μL ddH2O. PCR反应条件: 94℃预变性5 min.进行前20个循环: 94℃,1 min; 65-55℃,1 min; 72℃,1 min(其中每个循环后退火温度下降0.5℃).其次进行后10个循环: 94℃,1 min; 55℃,1 min; 72℃,1 min.最后72℃延伸8 min. PCR产物用1.5%琼脂糖凝胶电泳检测,并将电泳条带扫描拍照.
采用变性梯度凝胶电泳(DGGE)系统对总细菌PCR产物进行电泳分离.选用的聚丙烯酰胺凝胶浓度(丙烯酰胺:双丙烯酰胺为37.5 ∶1)为10%,变性梯度为40%-60%(其中100%的变性剂为7 mol ·L-1的尿素和40%的去离子甲酰胺的混合物).首先制备DGGE凝胶,待胶完全凝固后,将胶板放入装有电泳缓冲液的电泳槽.其次,取20 μL左右的PCR产物与5 μL左右的10×buffer混合均匀后进行上样,在每个加样孔加入含有10%的加样缓冲液的PCR样品25 μL.最后于60℃、 150 V下,电泳6 h.电泳完毕后,将凝胶进行SYBR Green I避光染色30 min左右并用超纯水润洗,其后将胶放入凝胶成像系统中拍照观察.
1.6 DGGE图谱分析利用Quantity One 7.0软件对DGGE图谱条带进行定量化.采用Shannon-wiener指数(H)评价不同阶段下连续流反应器中微生物群落的多样性. Shannon-wiener指数可用于反映群落种类的多样性,即群落种类越多,Shannon-Wiener指数值愈大,表示群落所含信息量就愈多.将图谱中包含的信息以二进制格式输出,利用Bio-dap软件计算Shannon-Wiener多样性指数. Shannon-Wiener指数的计算公式参考文献[20]提出的方法. 具体如下:
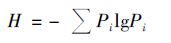
H的计算是基于电泳条带的位置和强度,而条带的峰面积可表示条带的强度.式中Pi=ni/N,其中,ni为峰面积,N为所有峰的总面积.
用SPSS 21.0对DGGE图谱进行聚类分析和主成分分析,以了解不同阶段下反应器中微生物的群落结构及其相似性.
1.7 微生物群落结构与环境因子的相关性分析典范对应分析(CCA)又称多元直接梯度分析,是基于对应分析发展而来的一种排序方法[21].将DGGE图谱中条带出现的地方标记为1,未出现的地方标记为0,对微生物群落结构与COD、 pH、NH4+-N、 NO2--N和NO3--N等环境因子的相关性进行典范对应分析.分析结果要借助国际通用软件Canoca 4.5进行排序.此外,在分析过程中需对所有环境因子进行标准化处理[22].
2 结果与讨论 2.1 反应器的运行图 2为反应器连续运行过程中各项出水指标的去除效果.从中可知,随着反应器的运行,COD、 NH4+-N、 NO2--N和NO3--N的去除率不断降低,18 d后各指标的去除率分别为98.1%、 96.4%、 92.0%和93.2%.其中6-14 d范围内各指标的去除速率均最快,分别达到67.3、 6.4、 2.5和1.9 mg ·(L ·d)-1.之后各指标的去除率均维持稳定.期间pH在7.1-7.3范围内波动,整体上呈微碱性,这可能与体系微生物代谢活动的硝化反硝化作用密切相关[23].总体上来说,经过18 d的运行反应器维持了较为稳定的去除效果.因此,选取前18 d运行周期内系统状态作为研究反应器从启动到稳定运行阶段系统内微生物群落结构的动态演替过程是适合的.

|
图 2 运行期间各出水指标的变化 Fig. 2 Change in indexes of outflow water during the operation |
采用试剂盒提取样品总DNA,经琼脂糖凝胶电泳检测后各样品总DNA的纯度和亮度较好,大小在23 kb左右,适合于下一步的PCR.采用细菌通用引物F357-GC、 R518对菌株16S rDNA V3区进行PCR扩增,将一部分扩增后的产物进行2.0%的琼脂糖凝胶电泳检测.通过对比,其分子量大小约在240 bp左右,确为扩增的目的条带.将另一部分扩增后的产物进行DGGE分析,结果如图 3所示.

|
图 3 污泥样品PCR产物变性梯度凝胶电泳 Fig. 3 DGGE profile of different PCR samples |
图 3给出了反应器连续运行18 d期间污泥样品的微生物群落结构.整个过程中微生物群落较为丰富,不同阶段之间微生物群落结构存在一定的差异性.其中S1有30条带、 S2有37条带、 S3有35条带,条带的数量波动不大,说明反应器运行的初期并没有立即造成群落多样性急剧降低. S4有28条带、 S5有18条带、 S6有36条带,条带的数量波动较大,表明体系内菌群发生了剧烈的竞争、 群落演替迅速,不适应环境的劣势菌群被大量淘汰,优势菌群开始出现并生长. S7有21条带、 S8有23条带、 S9有32条带,群落多样性有所回升,说明随着反应器的运行,体系内形成了新的菌群结构.此外,条带a、 d、 e、 k、 l随着反应器的运行,逐渐沦为劣势种群.条带c、 f、 i、 j出现在后期,为后续出现的新菌属.条带b、 g和h几乎始终存在于反应器中并在后期有所加强,所代表的是系统的优势菌群,这些菌株适应环境的能力较强,对反应器的稳定运行至关重要,筛选出这类优势菌对于加快反应器的启动、 提高反应器的容积负荷和处理效果均具有重要意义.其他条带变化没规律,对系统的稳定运行影响不大.这说明反应器的处理效果及稳定运行很大程度上与系统内微生物群落结构变化及演替过程有关.
图 4显示了以S1作为标准时各样品的DGGE图谱相似性分布.从中可知,各样品的相似性并不随着反应器的运行而呈比较有序的递减,微生物群落结构在运行期间经历了较大的变化. S6、 S7、 S8、 S9与S1相比,差别较大,相似性分别只有37.1%、 31.2%、 39.4%和41.9%,说明随着反应器的运行,微生物群落结构发生了较大的变化,这可能与反应器运行环境和条件的变化有一定联系.

|
图 4 污泥样品总细菌电泳条带相似性比较 Fig. 4 Similarity diagram of electrophoresis bands of total bacteria in different samples |
表 2给出了各阶段下污泥样品间菌群的相似性系数. 从中可知,S1-S2、 S2-S3至S8-S9,相邻阶段彼此间的相似性系数呈先上升后下降再上升的趋势.反应器启动时,体系内菌群结构因外界环境的冲击而受到一定的影响,S1-S2相似性仅为49.9%.随着反应器的运行,S2-S3相似性升高到62.5%,之后S3-S4相似性降低,其后继续下降,S5-S6相似性则降到最低,这可能是由于体系内菌群间的竞争作用,导致群落结构发生了剧烈的变化,劣势菌被大量淘汰,相邻阶段相似性出现急剧下降.运行后期相邻阶段相似性有所回升,S7-S8和S8-S9相似性分别恢复到49.4%和56.8%,说明反应器经过18 d的运行,微生物群落结构趋于稳定,接入的包埋菌可能适应了该体系并成为常驻优势菌.这也表明不同运行阶段下体系内微生物群落结构变化较大,污泥内菌群更替剧烈,劣势菌被大量淘汰.总的来说,DGGE图谱的相似性分布比较好地反映了微生物群落结构随反应器运行的变化关系.
|
|
表 2 各阶段污泥样品间菌群结构的相似性系数 /% Table 2 Similarity coefficient of profiles of the bacterial community structure in different stages/% |
通过Quantity One软件对DGGE图谱中条带的强度进行分析,再根据Shannon-Wiener多样性指数计算公式可得到总细菌的Shannon-Wiener多样性指数,结果见图 5.从中可知,在反应器的整个运行过程中,Shannon-Wiener指数的变化与反应器的运行有很大的关联,各阶段样品间多样性指数差异显著.整体上呈先下降后上升的趋势,反应器初始运行阶段,包埋菌在运行过程中要主动适应外界环境和营养条件,此时群落结构并未开始发生明显的变化,细菌群落多样性指数较高,S2最高可达到3.55.随着反应器的继续运行,菌株要不断融入新环境,彼此间的竞争加剧,多样性不断降低,群落结构发生根本性的变化,劣势菌大量死亡,包埋菌开始增殖.运行后期多样性呈上升的趋势,可能是由于体系中出现了其它新的菌属,也可能是包埋菌已适应外部环境并成为优势菌,体系内形成了新的菌群结构,多样性指数得到恢复.这表明不同运行阶段对微生物群落多样性有较大的影响,但微生物群落能通过自我调整来适应环境的变化.

|
图 5 各样品细菌的Shannon-Wiener多样性指数 Fig. 5 Shannon-Wiener index of the bacteria in different sludge samples |
不同统计学分析模型有时会导致得到的结果不一致.因此,选择合适的统计学方法是能否正确分析问题的关键[24].对不同阶段下污泥样品进行聚类分析能较好地反映微生物群落结构的变化与反应器运行的联系.
由图 6可知,通过UPGMA聚类分析可将DGGE图谱分为3类独立的群,其中S7、 S8和S9为第一族群,S1和S2为第二族群,S3、 S4、 S5和S6为第三族群.这大致可将反应器的运行过程划分为3个时期,即初始期、 竞争期和后期.说明随着反应器的运行,体系内的群落结构呈现有序的演替,这与张斌等的研究结论[25]相似. S1和S2作为运行初期,所含条带数较为接近,且菌群结构与其它时期有较大的区别,所以独立为一族. S3、 S4、 S5和S6单独作为一族,此阶段体系内菌群竞争加剧,使得演替过程最为激烈,菌群结构发生了根本性的变化.而S7、 S8和S9聚为一个族,处于运行后期,彼此间的相似性较高.此外,初始期和竞争期均处于不稳定运行阶段,与运行后期的相似性仅为0.37,说明不同运行阶段存在一定的演变关系,微生物群落经演替最终会形成稳定的菌群结构.

|
图 6 总细菌DGGE图谱的UPGMA聚类分析 Fig. 6 Cluster analysis of bacterial DGGE by UPGMA |
将DGGE图谱标准化后作主成分分析,主成分分析能反映微生物群落结构和功能的多样性变化[26, 27].经分析(见表 3),共提取出3个主成分,其所占的贡献率为83.1%,基本上能把不同阶段下的污泥样品中微生物群落结构区分开来.其中,S9与主成分一呈高度的正相关,S1、 S5和S7与主成分二呈高度的正相关,S2、 S3、 S4、 S6和S8与主成分三呈高度的正相关.
|
|
表 3 不同阶段微生物群落结构的主成分得分 Table 3 Principal component scores of microbial community structure in different stages |
图 7显示了每个条带在主成分上的因子载荷,条带(a、 c、 e、 f、 i、 j)在主成分一上的得分较高,主成分一是它们的代表因子,其中条带(c、 f、 i、 j)表征的是体系内出现的新菌群,说明反应器运行后期,体系内出现了新菌群,导致微生物菌群的数量在不断增多,多样性指数不断上升.条带(b、 g、 h)在主成分二上的载荷值较高,主成分二是它们的代表因子,这些条带几乎始终存在于反应器中并在后期有所加强,代表的是体系内的优势菌群(可能是包埋菌Burkholderia sp. YX02,也可能是体系内的土著优势菌),说明在反应器运行的整个过程中,这些菌株适应环境的能力较强,能够始终维持较旺盛的生命力,对反应器的稳定高效运行至关重要.条带(d、 k、 l)在主成分三上的载荷值较高,主成分三是它们的代表因子,这些条带代表的是体系内的劣势种群,随着反应器的运行,这些菌株会逐渐被淘汰,尤其在竞争期该现象将更加明显.因此,综合主成分分析的结果可知,随着反应器的运行,劣势菌被大量淘汰、 优势菌常驻,运行后期形成以包埋菌Burkholderia sp. YX02为代表的新的菌群结构.

|
图 7 不同样品中条带的载荷因子贡献 Fig. 7 PCA showing loading values for different samples |
采用典范对应分析法分析了微生物群落结构与环境因子的相关性.微生物群落结构与环境因子的相关性结果分别见表 4和图 8.
|
|
表 4 典范对应分析结果 Table 4 Results of Canonical correspondence analysis |

|
图 8 菌群结构多样性分布与环境因子的CCA排序 Fig. 8 CCA bioplot of distribution of the bacterial structure diversity and environmental variables |
由表 4可知,CCA分析前两轴的特征值分别为0.067和0.043,种与环境因子前两个排序轴的相关系数分别高达0.968和0.905,说明微生物群落结构和所选的环境因子间存在着很强的相关性.同时,第一排序轴解释了样本中22.1%的变异,第二和第三排序轴分别解释了样本中14%和10.8%的变异,前4个排序轴共解释了样本总变异的54.1%.而根据Gauch[28]的解释,虽然排序图仅能解释一小部分总变异,但也蕴涵丰富的信息.因此,该排序图基本能反映细菌群落与环境因子之间的关系.由图 8可知,在所有的环境因子中,NO2--N与第1排序轴呈负相关且相关程度最大,相关系数为-0.816 3,其次是NO3--N、 NH4+-N、 COD.所有变量均与第2排序轴正相关,与第二排序轴相关性最大的是NH4+-N,相关系数为0.475 4,其次是COD、 NO2--N、 NO3--N,而pH与第1、 2排序轴的相关系数均最小,分别为0.429 5和0.212 5.因此,对体系中微生物群落结构影响最大的是NO2--N,其次是NO3--N、 NH4+-N、 COD,pH影响最小.范艳君等[29]的研究结果表明氮素对水体中微生物群落结构影响很大. 有研究结果也表明限制淡水湖泊中微生物群落结构主要因素既含无机的营养物也含有机碳[30, 31].因此,微生物的群落结构不仅受到生物因素的调控,也与非生物因素(如环境因子等)的影响密不可分[32, 33].该结论启示人们在反应器实际运行的过程中,有效控制进水中含氮物质和COD的浓度对于反应器的稳定运行和提高处理效率具有重要的指示意义.
3 结论(1) 包埋固定化异养硝化-好氧反硝化菌Burkholderia sp. YX02强化连续流反应器在运行期间微生物群落较为丰富,不同阶段群落结构存在一定的差异性,运行期间体系内菌群处于动态变化中并最终形成稳定的结构.不同阶段群落结构的相似性并不随着反应器的运行而有序递减,群落结构经历了较大的变化,相邻阶段群落结构的相似性先下降后上升,群落结构经剧烈竞争后趋于稳定.多样性指数的变化与反应器的运行显著关联,各阶段之间多样性指数差异明显,运行后期出现了新的菌群.
(2) 包埋固定化异养硝化-好氧反硝化菌Burkholderia sp. YX02强化连续流反应器运行全过程大致可划分为3个时期,且不同时期存在一定的演变关系.随着反应器的运行,劣势菌大量淘汰、 优势菌常驻,运行后期形成以包埋菌Burkholderia sp. YX02为代表的新的菌群结构.
(3) 不同环境因子对包埋固定化异养硝化-好氧反硝化菌Burkholderia sp. YX02强化连续流反应器中微生物群落结构的影响不同,其中NO2--N的影响最大,其次为NO3--N、 NH4+-N、 COD,pH影响最小.在连续流反应器实际运行过程中,有效控制进水中含氮物质和COD的浓度可使反应器稳定运行及提高处理效果.
| [1] | 张光明, 杜锋伟, 朱易春, 等. A2/O生物同步脱氮除磷及其改良工艺进展[J]. 黑龙江大学自然科学学报, 2010, 27 (6): 739-742. |
| [2] | 张嘉超, 曾光明, 喻曼, 等. 农业废物好氧堆肥过程因子对细菌群落结构的影响[J]. 环境科学学报, 2010, 30 (5): 1002-1010. |
| [3] | Miyatake F, Iwabuchi K. Effect of high compost temperature on enzymatic activity and species diversity of culturable bacteria in cattle manure compost[J]. Bioresource Technology, 2005, 96 (16): 1821-1825. |
| [4] | 高孟春, 梁方圆, 杨丽娟, 等. PCR-DGGE解析阴离子交换膜生物反应器反硝化过程中微生物群落结构变化[J]. 中国海洋大学学报, 2010, 40 (4): 79-84. |
| [5] | 郭昱廷, 彭剑峰, 宋永会, 等. 温度对ABR反应器处理效果和微生物群落结构的影响[J]. 环境科学学报, 2012, 32 (7): 1542-1548. |
| [6] | 高秀红. A/O膜生物反应器中微生物群落的演替及对膜污染的影响[D]. 哈尔滨: 东北林业大学, 2011. |
| [7] | 满鹏, 齐鸿雁, 呼庆, 等. 利用PCR-DGGE分析未开发油气田地表微生物群落结构[J]. 环境科学, 2012, 33 (1): 305-313. |
| [8] | 李海红, 巴琦玥, 闫志英, 等. 不同原料厌氧发酵及其微生物种群的研究[J]. 中国环境科学, 2015, 35 (5): 1449-1457. |
| [9] | Wirth R, Kovács E, Maróti G, et al. Characterization of a biogas-producing microbial community by short-read nextgeneration DNA sequencing[J]. Biotechnology for Biofuels, 2012, 5 : 41. |
| [10] | Ács N, Kovács E, Wirth R, et al. Changes in the archaea microbial community when the biogas fermenters are fed with protein-rich substrates[J]. Bioresource Technology, 2013, 131 : 121-127. |
| [11] | 韩睿, 陈来生, 李莉, 等. PCR-DGGE研究青海农村户用沼气池微生物群落结构[J]. 中国环境科学, 2015, 35 (6): 1794-1804. |
| [12] | Calli B, Mertoglu B, Roest K, et al. Comparison of long-term performances and final microbial compositions of anaerobic reactors treating landfill leachate[J]. Bioresource Technology, 2006, 97 (4): 641-647. |
| [13] | Rowan A K, Snape J R, Fearnside D, et al. Composition and diversity of ammonia-oxidising bacterial communities in wastewater treatment reactors of different design treating identical wastewater[J]. FEMS Microbiology Ecology, 2003, 43 (2): 195-206. |
| [14] | 孙寓姣, 左剑恶, 李建平, 等. 厌氧颗粒污泥中微生物种群变化的分子生物学解析[J]. 中国环境科学, 2006, 26 (2): 183-187. |
| [15] | 邵基伦, 曹刚, 李紫惠, 等. 包埋固定化异养硝化菌强化处理氨氮有机废水[J]. 中国给水排水, 2015, 31 (1): 5-9. |
| [16] | Zhou J, Bruns M A, Tiedie J M. DNA recovery from soils of diverse composition[J]. Applied and Environmental Microbiology, 1996, 62 (2): 316-322. |
| [17] | 孙宝盛, 张斌, 吴卿, 等. 应用PCR-DGGE技术解析MBR中微生物群落多样性[J]. 天津大学学报, 2008, 41 (3): 356-361. |
| [18] | Muyzer G, de Waal E C, Uitterlinden A G, et al. Profiling of complex microbial populations by denaturing gradient gel electrophoresis analysis of polymerase chain reaction amplified genes coding for 16S rRNA[J]. Applied and Environmental Microbiology, 1993, 59 (3): 695-700. |
| [19] | 陈谊, 孙宝盛, 黄兴, 等. 膜生物反应器中不同阶段微生物群落结构演变的研究[J]. 环境工程学报, 2009, 3 (6): 1023-1028. |
| [20] | Shannon C E, Weaver W. The mathematical theory of communication[M]. Urbana, IL: University of Illinois Press, 1963. |
| [21] | 李永念, 左丽, 唐俊杰, 等. 贵阳市区及近郊三条主要河流细菌污染调查[J]. 贵阳医学院学报, 1997, 22 (3): 246-248. |
| [22] | 虞泳, 曾光明, 陈耀宁, 等. 农业废物好氧堆肥中氨氧化细菌的群落结构[J]. 环境科学, 2011, 32 (10): 3067-3072. |
| [23] | Yannarell A C, Triplett E W. Geographic and environmental sources of variation in lake bacterial community composition[J]. Applied and Environmental Microbiology, 2005, 71 (1): 227-239. |
| [24] | 储昭瑞. 厌氧氨氧化反应器启动及微生物群落结构解析[D]. 哈尔滨: 哈尔滨工业大学, 2012. |
| [25] | 张斌, 孙宝盛, 季民, 等. MBR中微生物群落结构的演变与分析[J]. 环境科学学报, 2008, 28 (11): 2192-2199. |
| [26] | 郑华, 欧阳志云, 方治国, 等. BIOLOG在土壤微生物群落功能多样性研究中的应用[J]. 土壤学报, 2004, 41 (3): 456-461. |
| [27] | Glimm E, Heuer H, Engelen B, et al. Statistical comparisons of community catabolic profiles[J]. Journal of Microbiology Methods, 1997, 30 (7): 71-80. |
| [28] | Gauch H G Jr. Multivariate analysis in community ecology[M]. New York: Cambridge University Press, 1982. |
| [29] | 范艳君, 朱玲, 朱伟, 等. 珠江口颗粒附着微生物群落沿环境梯度的演替[J]. 渔业科学进展, 2012, 33 (3): 8-14. |
| [30] | Rivkin R B, Anderson M R. Inorganic nutrient limitation of oceanic bacterioplankton[J]. Limnology and Oceanography, 1997, 42 (30): 730-740. |
| [31] | Øvreås L, Bourne D, Sandaa R A. Response of bacterial and viral communities to nutrient manipulations in sea-water mesocosms[J]. Aquatic Microbial Ecology, 2003, 31 (2): 109-121. |
| [32] | 王丽梅. 环境因子对抗性基因消长动力学及耐药微生物群落结构变化的影响研究[D]. 天津: 南开大学, 2011. |
| [33] | 章燕平. 环境因素对菜地土壤氮素转化及其生物学特性的影响[D]. 杭州: 浙江大学, 2010. |
 2016, Vol. 37
2016, Vol. 37


